Analyse protéomique par spectrométrie de masse
PRÉSENTATION
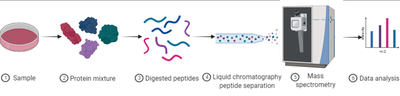
La protéomique permet d’identifier, de caractériser, de quantifier des protéines dans un échantillon biologique. L’analyse protéomique est applicable à de nombreux domaines : santé, environnement, agronomie etc... Une analyse protéomique se déroule en différentes étapes : la première consiste à extraire les protéines de l’échantillon biologique que l’on souhaite étudier. Ensuite on digère les protéines à l’aide d’une enzyme (comme la trypsine) pour obtenir un mélange peptidique. Ce mélange est alors analysé par chromatographie liquide couplée à un spectromètre de masse afin d’obtenir des spectres de fragmentation peptidique. L’ensemble des données est alors comparé à des banques de données protéiques à l’aide de logiciels bioinformatiques pour identifier les protéines présentes dans l’échantillon.
PRESTATIONS
Le pôle de Spectrométrie de Masse propose en prestation ou en collaboration, les services suivants :
- Identification et analyse de mélanges complexes de protéines
- Caractérisation de modifications post-traductionnelles (Phosphorylation, Acétylation…)
- Quantification relative de protéines dans des mélanges complexes (comparaison de différentes conditions) par des approches de marquage (TMT) ou par approche label free (LFQ)
- Recherche de partenaires après immunoprécipitation
- Etudes structurales sur protéine entière
- Mesure de masse moléculaire de petites molécules, peptides, de protéines d’oligonucléotides ou de polymères de synthèse : par MALDI/TOF ou ESI/Orbitrap après déconvolution d’ions multichargés.
- Développement d’outils bioinformatiques pour l’aide à l’exploitation des données protéomiques
Préparation d’échantillon
Nous prenons en charge des échantillons compris dans une gamme large de concentration (du µg au mg) et issus de préparations très diverses (gel, liquide, sur billes, extrait sec).
Nous assurons les étapes de préparation des échantillons avant l’analyse par spectrométrie de masse :
- Digestion enzymatique (différentes protéases)
- Etape d’enrichissement pour la caractérisation de modifications post-traductionnelles
- Etape de marquage isotopique (TMT, Dimethyl tag) pour la quantification relative
- Fractionnement
- Dosage peptidique par fluorescence
- Dessalage
Traitement de données
Logiciels d’analyse :
Différents logiciels d’analyse de données sont utilisés pour le retraitement des données protéomiques :
- Proteome Discoverer 2.5 et 3.1 avec Chimerys (Thermo Scientific) : données DDA
- Biopharma Finder 3.1 (Thermo Scientific) : peptide mapping, protéine entière
- Skyline : données PRM
Pour l’étude plus approfondie de vos données de protéomique, le support bioinformatique développe des outils pour la visualisation et l’exploitation des données. Par exemple, un outils web permet d’explorer interactivement des données de protéomique quantitative et de lancer des analyses d’enrichissement.
Dépôt et sauvegarde des données :
Toutes les données sont sauvegardées sur nos serveurs pour une durée de 5 ans. Au-delà les données sont archivées.
Nous prenons en charge sur demande la soumission des données sur les serveurs publics (PRIDE ou MassIVE) lors de la soumission d'article.
Demande d’analyse
Pour soumettre une demande d’analyse, merci de remplir la fiche échantillon MS et l’apporter avec vos échantillons ou nous l’envoyer par mail (protein.science@ibcp.fr) :
ÉQUIPEMENTS
Le service est équipé de 3 spectromètres de masse :
|
Q Exactive HF Biopharma couplé à une nanoRSLC (Thermo Scientific) :
|
 |
|
VOYAGER De Pro (Sciex) :
|
 |
|
Exploris 480 (à droite) couplé à la nanoLC Vanquish NEO (à gauche) (Thermo Scientific) :
|
 |


